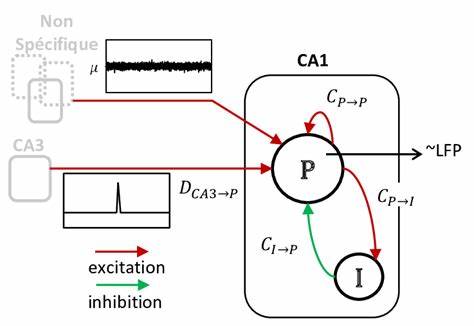
生物数学作为连接生物学与定量分析的桥梁,近年来在生命科学研究中发挥着愈发重要的作用。随着高通量测序、质谱分析和大规模实验技术的普及,生物系统产生的数据量和复杂性呈指数级增长。在这样的背景下,如何将复杂的生物网络以结构化方式表示、有效地在海量图数据中进行检索和匹配,成为研究者面临的核心挑战之一。EPFL(洛桑联邦理工学院)在图搜索领域的研究与工具开发,提供了面向生物网络分析的先进思路与可操作平台,帮助科研人员将拓扑信息、功能标注与实验数据融合,用图搜索来发现新的生物学模式与假说。 首先理解图搜索在生物学中的价值尤为重要。生物分子之间的关系天然适合用图来建模:蛋白质相互作用网络、代谢通路、基因调控网路、细胞间通讯网络、生态互作网络等都可以表示为节点与边的结构。
图搜索的核心任务是从大规模数据库中按结构或属性匹配子图,快速定位与给定查询相似或同构的网络片段。对生物学家而言,这意味着可以在不同物种、不同实验条件或不同数据库中,找到具有相同拓扑特征或功能模块的网络区域,从而推断保守机制、预测未知交互或验证实验结果。 EPFL在Graph Search方面的研究强调效率与可扩展性。生物网络的规模和复杂性远超过传统小型图的范畴,常常需要处理成千上万节点与数十万边的图。为此,图搜索系统需要在索引构建、子图匹配算法、并行计算与内存管理上做大量优化。常见的技术路径包括基于压缩索引的快速候选集生成、利用图特征滤波大幅减少精确匹配的搜索空间、采用启发式或约束传播的方法快速排除不匹配分支,以及结合图嵌入技术进行近似匹配以应对噪声和不完全数据。
EPFL提出的方案往往将算法创新与工程实现结合,既重视理论复杂度,也关注实际运行时的扩展能力。 在生物学实际应用场景中,Graph Search有多种重要用途。蛋白质相互作用网络(PPI)是最直观的例子。研究者可以以已知的蛋白质复合体或功能模块作为查询,在PPI数据库中搜索结构上相似的子网络,从而发现不同物种或不同细胞类型中可能执行相同功能的蛋白质组。基因调控网络中,转录因子与其靶基因之间的调控模式常常形成特定的网络动机(motif),图搜索能够系统地定位这些motif并比较其在不同条件下的富集情况,帮助理解调控层次与信号传导路径。另外,在系统生物学与代谢工程领域,代谢通路的拓扑模式与物质流动路径的结构查找同样依赖高效的图搜索,以便识别可替换路径或潜在的工程改造点。
流行病建模与传播网络分析是另一个受益于图搜索的领域。疾病传播网络通常以个体或群体为节点,传播路径为边,通过图搜索可以识别超级传播者(super-spreaders)、高风险传播链条或易受攻击的网络结构,从而为干预策略提供依据。结合时间序列信息的动态图搜索进一步支持在不同时间窗口下比较传播拓扑的演化,有助于评估防控措施的效果。 从工具与数据格式的角度看,EPFL Graph Search关注互操作性与可复现性。生物网络数据通常来源多样,常见格式包括GraphML、GEXF、SIF、TSV边列表以及基于RDF/OWL的语义网络。一个成熟的图搜索平台需要支持这些多种输入格式,并提供清晰的数据转换管道以保留节点属性、边属性与注释信息。
同时,为了便于下游分析,工具还应支持将搜索结果导出为常用格式,或与数据库(例如Neo4j、OrientDB、ArangoDB等图数据库)以及生物信息学平台(如Cytoscape)集成,使研究流程连贯、易于共享与复现。 对搜索算法而言,子图同构与近似匹配是两大主要问题。子图同构关注精确匹配,要求找到与查询图在结构与属性上完全一致的子图;这在检测保守复合体或严格定义的功能模块时非常重要,但计算复杂度高,通常是NP难问题。为提升效率,EPFL的研究会结合多级索引、节点标签分级过滤、以及基于邻域特征编码的候选筛选策略,显著降低回溯搜索的分支数。近似匹配则更贴合生物数据的现实 - - 实验噪声、注释缺失或进化改动都会导致完全同构难以存在。图嵌入、图核方法与编辑距离度量为近似匹配提供了可行路径,允许系统以容忍一定差异的方式评估结构相似性,从而在实际研究中更有用。
一个高质量的Graph Search平台还需要良好的可视化能力。网络结构的可视化不仅帮助研究者直观理解匹配结果,还能用于探索性分析与假说生成。交互式可视化支持节点与边的动态筛选、高亮路径追踪、属性映射(如表达量或功能注释)以及动画展示时间序列网络的演化。EPFL工具往往结合现代前端可视化库,提供浏览器端交互界面,同时支持导出静态图像或可交互结果以便发表与共享。 安全性与访问性的考虑在公共在线服务中不可忽视。用户访问图搜索平台时,可能会遇到像Cloudflare这样的安全验证页面,这是为了防止恶意流量并保障平台稳定运行。
对科研用户来说,重要的是了解平台的访问策略、数据隐私保护措施以及如何通过API密钥或机构访问来提高请求的可靠性。对于托管敏感数据的项目,建议在本地或私有云环境中部署Graph Search实例,以便对数据访问与计算资源进行严格管理。 使用EPFL Graph Search进行实际研究时,有若干最佳实践值得推荐。首先,数据预处理至关重要。清洗与标准化节点/边注释、去除冗余或低质量的交互、统一命名空间(如Gene Ontology、UniProt标识)可以显著提升匹配质量与结果可解释性。其次,合理选择匹配策略:对需要精确结构证据的问题采用子图同构,对更关注功能相似性或进化保守性的场景采用近似匹配或图嵌入方法。
再次,混合使用拓扑信息与节点属性常常能提高判别力,例如在匹配时同时考虑邻域结构与蛋白质的功能注释或表达谱相似度。最后,进行统计验证与后验分析是不可或缺的步骤,通过随机化网络或基于空模型的富集分析来评估匹配结果的显著性,避免过度解读偶然匹配。 案例研究有助于将抽象概念具体化。想象一个研究团队希望在人类与酵母的PPI数据库中寻找功能保守的蛋白质复合体。他们可以以在酵母中验证过的复合体拓扑作为查询,在人类PPI网络中通过图搜索定位拓扑相似的子图,并结合序列相似性与功能注释来筛选候选复合体。进一步,他们可以使用表达数据评估在相近条件下这些候选复合体是否共表达,从而判断是否可能具有相似功能。
另一个例子是药物重定位,通过将药物作用靶点构建为小型图结构,搜索在人类疾病网络中与该结构相似的网络片段,可能揭示药物对不同病理过程的潜在影响,从而提出新的治疗假设。 面向未来,图搜索在生命科学中的潜力仍然巨大。随着单细胞技术、空间组学以及多组学数据的加入,生物网络将进一步扩展为多层、多尺度的图模型。跨层次的图搜索能力,将允许研究者在基因、蛋白、代谢与细胞层面上同时进行模式匹配,揭示复杂表型背后的综合网络逻辑。人工智能与深度学习的发展也将推动图嵌入与图神经网络在匹配任务中的应用,使得对功能相似性与潜在因果关系的捕捉更加敏感与鲁棒。 此外,开放科学与共享数据的趋势将推动构建更大规模的公共图数据库与可复现的搜索工作流。
标准化的数据格式、可追溯的索引构建过程以及透明的统计验证方法,将是提升研究可信度的关键。EPFL在学术界的桥梁作用,有助于将前沿算法快速转化为可重复使用的工具,并通过教学与社区建设培养更多既懂生物学又精通算法的跨学科人才。 总之,在生命科学研究不断迈向大数据与系统化理解的时代,生物数学与图搜索结合提供了一种强有力的方法论。EPFL Graph Search所体现的技术方向 - - 高效索引、可扩展的匹配算法、可视化与可复现的工作流 - - 正是推动这一领域进步的关键要素。对于希望在蛋白互作、基因调控、代谢工程、流行病学和生态网络等领域开展深入网络分析的研究者,掌握图搜索的原理与工具、遵循数据规范并结合统计验证,将显著提升研究发现的质量与可验证性。未来,随着数据层次的丰富与计算方法的进化,图搜索将在揭示生命复杂性和发现新的生物学规律中扮演越来越重要的角色。
。